Projekt
ChitoPop
Optimierung der Pathogenresistenz und Mykorrhizierung von Pappeln durch Modifikation von LysM-Proteinen
Pappeln können Schadpilze über Rezeptoren erkennen, die spezifisch an das Chitin, einem Bestandteil der Zellwand vieler Pilze, binden. Die Wahrnehmung des Chitins löst in Pappeln eine Immunantwort aus, die zu einer Resistenz gegen den Eindringling führen kann. In diesem Projekt sollen die hierbei beteiligten Gene charakterisiert werden. Darüber hinaus soll die Pappel in ihrer Fitness gestärkt werden, indem Pilze, die Wurzeln besiedeln und für das Wachstum förderlich sind (symbiontische Pilze; Mykorrhizapilze), gefördert werden (Mykorrhizierung).
Hintergrund und Zielsetzung
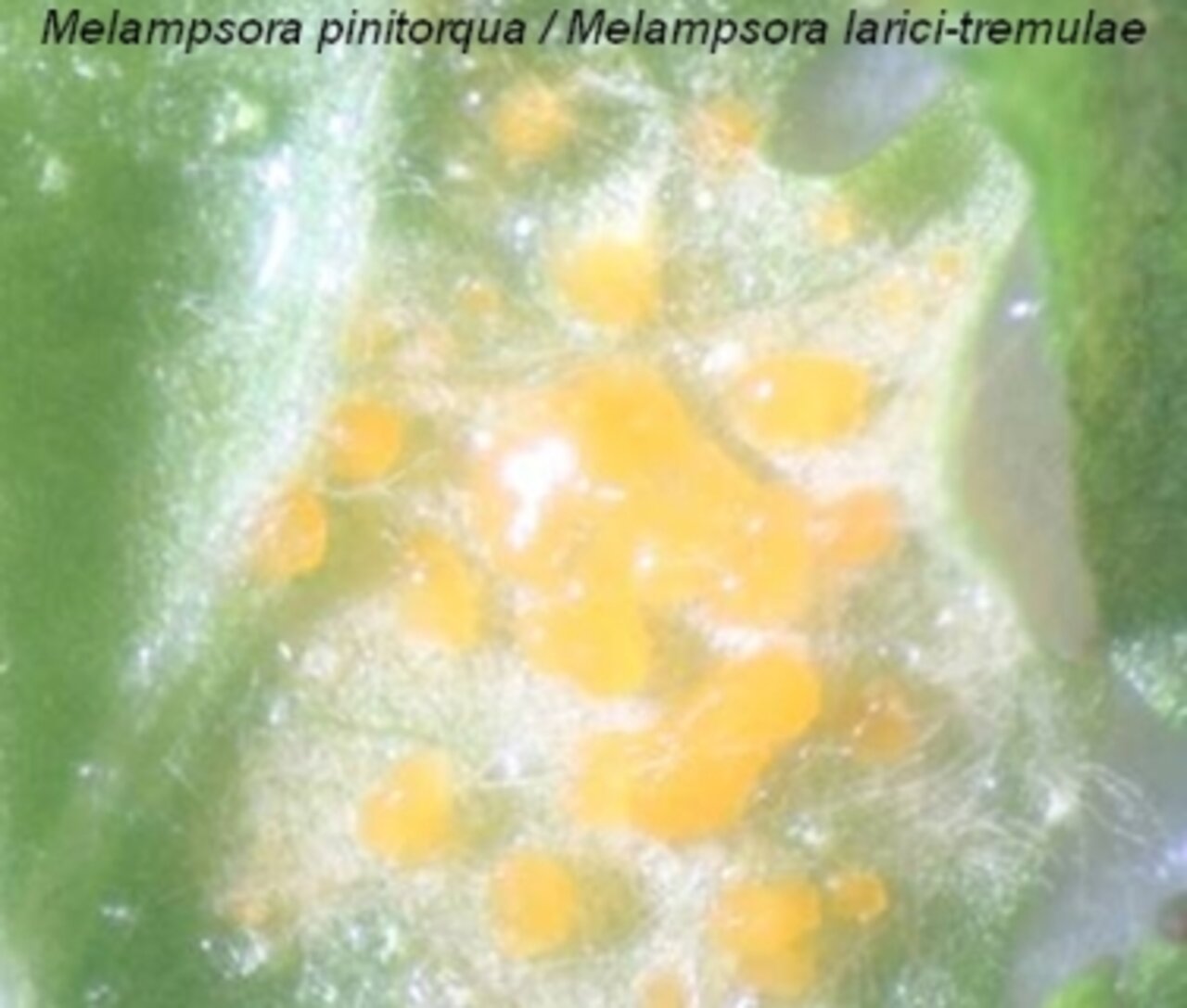
Pappeln werden in Kurzumtriebsplantagen für die Produktion von Bioenergie angebaut. Während der gesamten Zeit ist die Plantage ständig verschiedensten Pilzerregern ausgesetzt, die schwere Schäden an den Bäumen verursachen können. Die meisten dieser schädlichen Pilzerreger bei der Pappel sind Schadpilze der Gattung Melampsora. Insbesondere stellt die kosmopolitische Art M. larici-populina die größte Bedrohung für Pappelplantagen dar, die jährlich Wachstumseinbußen von bis zu 50 Prozent verursachen.
Das pflanzliche Immunsystem reagiert in einem Befall mit Schadpilzen mit einer Abwehrreaktion, die über einen komplexen molekularen Mechanismus vermittelt wird. Das pilzliche Chitin wird dabei zunächst über spezielle Rezeptoren erkannt. Die Wahrnehmung des Chitins löst in Pflanzen eine Immunantwort aus, die zu einer Resistenz gegen den Eindringling führen kann. Auf der anderen Seite müssen symbiontische Pilze diese Immunantwort umgehen oder unterdrücken, um eine Etablierung einer Mykorrhizierung zu erreichen. Ziel des Projektes ist es, in Pappeln die an dieser Abwehrreaktion beteiligten verschiedenen Komponenten zu identifizieren und funktionell zu charakterisieren. Zudem soll geklärt werden, wie die Pappel zwischen Schadpilzen und symbiontischen Pilzen unterscheiden kann. Damit sollen die Grundlagen dafür gelegt worden, die Pathogenresistenz und Mykorrhizierung von Pappeln zu optimieren.
Vorgehensweise
In diesem Projekt wollen wir Gene, die für LysM-RLKs-Rezeptoren in der Pappel und LysM-Effektoren in dem Mykorrhiza-Pilz Laccaria kodieren, identifizieren. Diese Gene sollen funktionell charakterisiert und in der Pappel getestet werden, um die Immunantwort und gleichzeitig den Mykorrhizierungsgrad der Pappel zu verbessern. Hierfür werden wir sowohl transgene Linien erzeugen als auch die CRISPR/Cas9-Technologie für eine gezielte Veränderung ausgewählter LysM-RLKs-Rezeptorgene anwenden.
Für die vom Projektpartner 1 per in silico Analyse in P. trichocarpa identifizierten Kandidatengene sowie deren Paraloge (Potri.005G128400 / Potri.007G032300 und Potri.008G160600 / Potri.010G078700) wurden homologe Sequenzen aus verfügbaren P1-Genomsequenzen bioinformatisch herausgefiltert.
Durch die mit dem CRISPR/Cas9 Konstrukt zur Modifikation in Potri.005G128400 und Potri.007G032300 konnten für Potri.005G128400 insgesamt 133 Regenerate erzeugt werden, von denen nach Analyse der Integrität des Konstruktes 113 unabhängig transgene Linien zur DNA-Sequenzierung verwendet wurden. Es ergab sich eine Verteilung von 62 heterozygot modifizierten Linien, 40 homozygot modifizierten Linien und 11 Linien, die dem Wildtyp entsprachen. Von den 40 homozygot modifizierten Linien traten 6 unterschiedliche Modifikationen auf. Im Verlauf der Arbeit zeigte sich, dass bei der Amplifikation dieser Linien nur eines der beiden Allele von P. × canescens amplifiziert wurde. Die Anzahl der Linien wurden leider im Vorfelde stark reduziert, sodass die noch vorhandenen Linien erneut auf eine Modifikation im zweiten Allel getestet werden mussten. Die ausgewählten Linien, für die eine Modifikation in Potri.005G128400 in einem der beiden Allele nachgewiesen werden konnte, zeigten dann ebenfalls eine Modifikation im zweiten Allel. Für eine der ausgewählten Linien war die Modifikation homozygot, für alle weiteren heterozygot biallelisch.
Diese Linien wurden zur phänotypischen Analyse in das Gewächshaus überführt. Weiterhin erfolgten RNA-Isolationen der ausgewählten Linien, um eine Modifikation auch auf cDNA- Ebene zu verifizieren. Hierzu wurde RNA aus Blatt und Wurzelmaterial isoliert, in cDNA umgeschrieben und mittels PCR amplifiziert. Es zeigte sich für Potri.005G128400, dass in cDNA aus Wurzeln die gleichen Modifikationen vorliegen, lediglich eine Linie wies eine zusätzliche Modifikation mit einer Deletion von 5 nt anstelle der Insertion eines Einzelnukleotides auf. Die cDNA Analyse aus Blattmaterial zeigte in 3 von 7 Linien überlagerte Chromatogramme, obwohl nur eines der beiden Allele amplifiziert wurde. Dieses deutet auf chimäre Strukturen hin. Derzeit wird über PCR Amplifikation überprüft, ob die erstellten cDNA-Proben ausschließlich auf RNA beruhen oder ob Kontaminationen mit DNA vorliegen. Zwei unabhängig in Potri.005G128400 modifizierte Linien wurden bereits für Mykorrhizierungsversuche an Projektpartner P3 (Dr. Stephanie Werner, Institut für Pflanzenbiochemie, Halle) übergeben.
Thünen-Ansprechperson

Thünen-Beteiligte
Beteiligte externe Thünen-Partner
- Georg-August-Universität Göttingen
(Göttingen, Deutschland)
Geldgeber
-
Bundesministerium für Forschung, Technologie und Raumfahrt (BMFTR)
(national, öffentlich)
Zeitraum
10.2016 - 10.2022
Weitere Projektdaten
Projektstatus:
abgeschlossen
Publikationen zum Projekt
- 0
Deecke K, Fladung M (2021) Melampsora-Resistenztests in Pappeln. AFZ Der Wald 76(4):26-29
- 1
Brügmann T, Polak O, Deecke K, Nietsch J, Fladung M (2019) Poplar transformation. Meth Mol Biol 1864:165-177
- 2
Fladung M, Ewald D (2018) Biotechnologie schnellwachsender Baumarten. In: Veste M, Böhm C (eds) Agrarholz - Schnellwachsende Bäume in der Landwirtschaft : Biologie - Ökologie - Management. Wiesbaden: Springer Spektrum, pp 147-168, DOI:10.1007/978-3-662-49931-3_6
- 3
Fladung M, Lipka V, Petutschnig E, Werner S, Teichmann T (2018) ChitoPop improvement of poplar pathogen response and mycorrhization by modification of LysM proteins. In: Conference Documents Plant 2030 Status Seminar 2018, February 5-7. pp 47-48
- 4
Bartsch D, Bendiek J, Bräuning A, Ehlers U, Dagand E, Duensing N, Fladung M, Franz C, Groeneveld E, Grohmann L, Habermann D, Hartung F, Keilwagen J, Leggewie G, Matthies A, Middelhoff U, Niemann H, Petersen B, Scheepers A, Tebbe CC, et al (2018) Wissenschaftlicher Bericht zu den neuen Techniken in der Pflanzenzüchtung und der Tierzucht und ihren Verwendungen im Bereich der Ernährung und Landwirtschaft : überarbeitete Fassung vom 23.02.2018 [online]. BVL; MRI; TI; BfR; FLI, 83 p, zu finden in <https://www.bmel.de/SharedDocs/Downloads/Landwirtschaft/Pflanze/GrueneGentechnik/Bericht_Neue_Zuechtungstechniken.pdf> [zitiert am 20.03.2018]
- 5
Fladung M (2017) Debate is failing Europe's geneticists. Nature 544:35